- Главная
- Химия
- Молекулярные базы данных. Принцип действия и характеристики основных компьютерных программ

Содержание
- 2. Новейшим методом изучения природных молекул является применение информационных систем. Работая с информационными моделями молекул, исследователь обычно
- 3. Компьютерным моделированием молекулярно-генетических и смежных процессов занимаются такие науки как биоинформатика, системная биология, геномика, эволюционная генетика,
- 4. Биоинформатика Биоинформатика — это область науки, разрабатывающая и применяющая вычислительные алгоритмы для систематизации и анализа генетической
- 5. Биоинформатика включает в себя: базы данных, в которых хранится биологическая информация набор инструментов для анализа тех
- 6. Задачи, решаемые биоинформатикой
- 7. Биолог в биоинформатике обычно имеет дело с базами данных и инструментами их анализа. Теперь разберемся, какие
- 8. Второй тип – курируемые базы данных, за достоверность которых отвечает хозяин базы данных. Туда информацию никто
- 9. Поддержание базы требует работы кураторов или аннотаторов. Тем не менее, даже в курируемых базах данных могут
- 10. Третий тип – производные базы данных. Такие базы получаются в результате обработки данных из архивных и
- 11. И интегрированные базы данных, в которых вся информация (курируемая, не курируемая) свалена в кучу, и введя
- 12. Теперь перейдем к рассмотрению инструментов биоинформатики. Инструменты определяются задачами, которые мы хотим решать. Основу биоинформатики составляют
- 13. Как сравнивают последовательности? Запишем одну последовательность под другой: attgtACcTCgTgG-AA---- -----AC-TCaTaGcAAccag Нам надо при сравнении найти наилучший
- 14. Таким образом, первым делом после секвенирования последовательности ищут в базах данных похожие последовательности, чтобы после сравнения
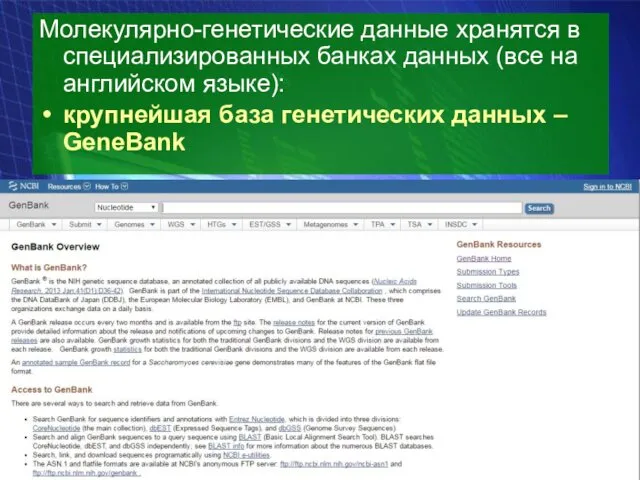
- 15. Молекулярно-генетические данные хранятся в специализированных банках данных (все на английском языке): крупнейшая база генетических данных –
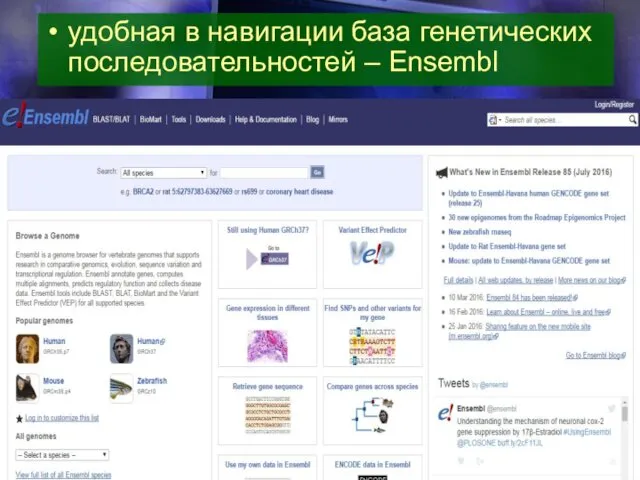
- 16. удобная в навигации база генетических последовательностей – Ensembl
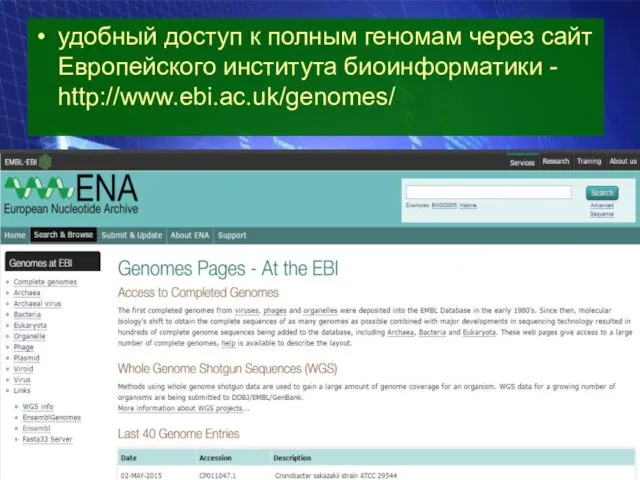
- 17. удобный доступ к полным геномам через сайт Европейского института биоинформатики - http://www.ebi.ac.uk/genomes/
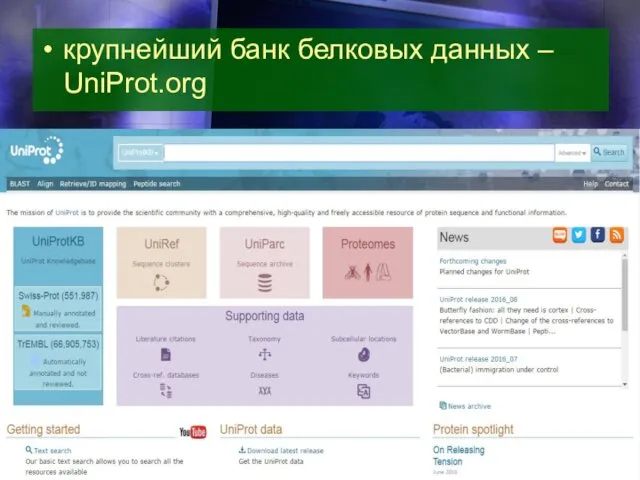
- 18. крупнейший банк белковых данных – UniProt.org
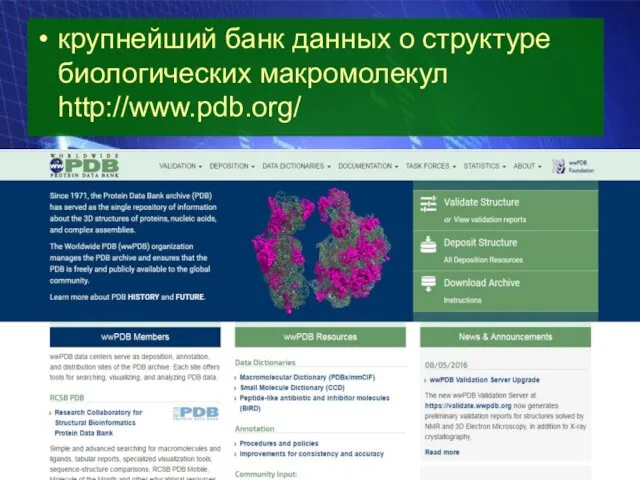
- 19. крупнейший банк данных о структуре биологических макромолекул http://www.pdb.org/
- 20. Информационные системы, касающиеся моделей макромолекул и надмолекулярных структур: GeneBank & EMBL – здесь хранятся первичные последовательности
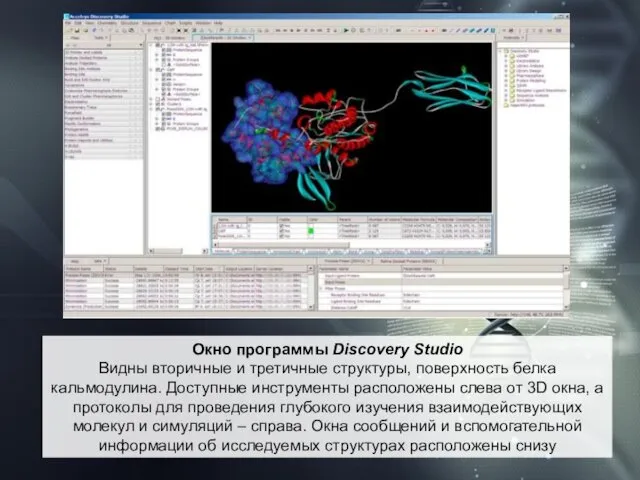
- 21. Окно программы Discovery Studio Видны вторичные и третичные структуры, поверхность белка кальмодулина. Доступные инструменты расположены слева
- 22. CAZy: Carbohydrate-Active Enzymes Database. На сайте представлена современная классификация ферментов синтеза и утилизации углеводов, а также
- 23. http://molbiol.edu.ru/review/01_01.html
- 29. Форматы файлов, используемых в биоинформатике FASTA >roa1_drome Rea guano receptor type III >> 0.1 MVNSNQNQNGNSNGHDDDFPQDSITEPEHMRKLFIGGLDYRTTDENLKAHEKWGNIVDVVVMKDPRTKRSRGFGFITYSHSSMIDEAQKSRPHKIDGRVEPKRAVPRQDIDSPNAGATVKKLFVGALKDDHDEQSIRDYFQHFGNIVDNIVIDKETGKKRGFAFVEFDDYDPVDKVVLQKQHQLNGKMVDVKKALPKNDQQGGGGGRGGPGGRAGGNRGNMGGGNYGNQNGGGNWNNGGNNWGNNRGNDNWGNNSFGGGGGGGGGYGGGNNSWGNNNPWDNGNGGGNFGGGGNNWNGGNDFGGYQQNYGGGPQRGGGNFNNNRMQPYQGGGGFKAGGGNQGNYGNNQGFNNGGNNRRY >roa2_drome
- 30. GenBank LOCUS SCU49845 5028 bp DNA PLN 21-JUN-1999 DEFINITION Saccharomyces cerevisiae TCP1-beta gene, partial cds, and
- 31. GenBank. Запись sequence
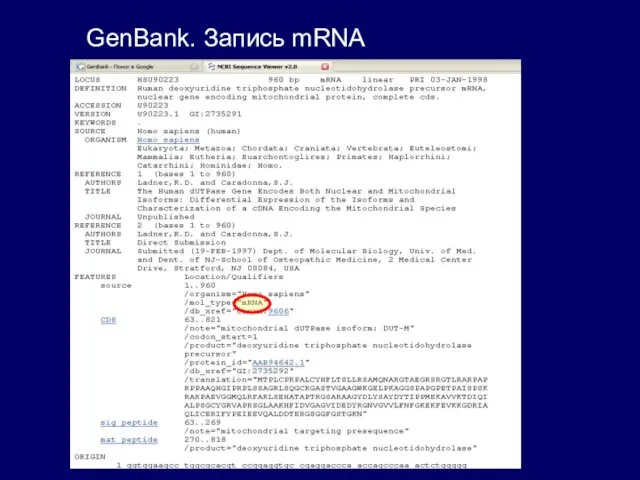
- 32. GenBank. Запись mRNA
- 33. Сплайсинг и восстановление последовательности mRNA mRNA seq=(AF018429.1:282-561)+(AF018429.1:1034-1172)+(AF018430.1:560-651)+(AF018430.1:1-45)+………
- 34. GenBank. Запись genomic DNA
- 35. GenBank. Аннотация
- 36. Как добавить данные в GB? http://www.ncbi.nlm.nih.gov/ Genbank/submit.html Зачем? информация в community; Журналы требуют это ДО публикации
- 37. Форматы описания белков PDB PDB-XML MMDB-Cn3D
- 38. PDB – Protein Data Bank HEADER LUMINESCENT PROTEIN 09-DEC-03 1RRX TITLE CRYSTALLOGRAPHIC EVIDENCE FOR ISOMERIC CHROMOPHORES
- 39. HELIX 1 1 GLU A 5 THR A 9 5 5 HELIX 2 2 ALA A
- 40. PDB-XML PDBML: the representation of archival macromolecular structure data in XML. John Wesbrook, Nobutoshi Ito, Haruki
- 42. Скачать презентацию
Новейшим методом изучения природных молекул является применение информационных систем.
Работая с
Новейшим методом изучения природных молекул является применение информационных систем.
Работая с
Компьютерным моделированием молекулярно-генетических и смежных процессов занимаются такие науки как биоинформатика,
Компьютерным моделированием молекулярно-генетических и смежных процессов занимаются такие науки как биоинформатика,
Биоинформатика
Биоинформатика — это область науки, разрабатывающая и применяющая вычислительные алгоритмы для
Биоинформатика
Биоинформатика — это область науки, разрабатывающая и применяющая вычислительные алгоритмы для
Биоинформатика возникла в 1976-1978 годах, окончательно оформилась в 1980 году со специальным выпуском журнала «Nucleic Acid Research» (NAR).
Биоинформатика включает в себя:
базы данных, в которых хранится биологическая информация
набор инструментов
Биоинформатика включает в себя:
базы данных, в которых хранится биологическая информация
набор инструментов
правильное применение компьютерных методов для правильного решения биологических задач
Задачи, решаемые биоинформатикой
Задачи, решаемые биоинформатикой
Биолог в биоинформатике обычно имеет дело с базами данных и инструментами
Биолог в биоинформатике обычно имеет дело с базами данных и инструментами
Первый тип – архивные базы данных, это большая свалка, куда любой может поместить все, что захочет. К таким базам относятся:
GeneBank & EMBL – здесь хранятся первичные последовательности
PDB – пространственные структуры
В качестве курьеза можно привести пример: в архивной базе данных указано, что в геноме археи (архебактерии) есть ген, кодирующий белок главного комплекса гистосовместимости, что является полной чепухой, т.к. характерно для позвоночных.
Второй тип – курируемые базы данных, за достоверность которых отвечает хозяин
Второй тип – курируемые базы данных, за достоверность которых отвечает хозяин
К базам данных такого типа относятся:
Swiss- Prot – наиболее качественная база данных, содержащая аминокислотные последовательности белков
KEGG – информация о метаболизме
FlyBase – информация о Drosophila
COG – информация об ортологичных генах (гомологичные гены филогенетически родственных организмов, разошедшихся в процессе видообразования)
Поддержание базы требует работы кураторов или аннотаторов. Тем не менее, даже в
Поддержание базы требует работы кураторов или аннотаторов. Тем не менее, даже в
CAUTION: AN ORF CALLED DSDC WAS ORIGINALLY (REF.3) ASSIGNED TO THE WRONG DNA STRAND AND THOUGHT TO BE A D- SERINE DEAMINASE ACTIVATOR, IT WAS THEN RESEQUENCED BY REF.2 AND STILL THOUGHT TO BE "DSDC", BUT THIS TIME TO FUNCTION AS A D-SERINE PERMEASE. IT IS REF.1 THAT SHOWED THAT DSDC IS ANOTHER GENE AND THAT THIS SEQUENCE SHOULD BE CALLED DSDX. IT SHOULD ALSO BE NOTED THAT THE C-TERMINAL PART OF DSDX (FROM 338 ONWARD) WAS ALSO SEQUENCED (REF.6 AND REF.7) AND WAS THOUGHT TO BE A SEPARATE ORF (YES, DON'T WORRY, WE ALSO HAD PROBLEMS UNDERSTANDING WHAT HAPPENED!).
По крайне мере здесь кураторы базы данных честно признаются, что не знают, как это случилось.
Третий тип – производные базы данных. Такие базы получаются в результате
Третий тип – производные базы данных. Такие базы получаются в результате
SCOP – База данных структурной классификации белков (описывается структура белков)
PFAM – База данных по семействам белков
GO (Gene Ontology) – Классификация генов (попытка создания набора терминов, упорядочивания терминологии, чтобы один ген не назывался по разному, и чтобы разным генам не давали одинаковые названия)
ProDom – белковые домены
AsMamDB – альтернативный сплайсинг у млекопитающих
И интегрированные базы данных, в которых вся информация (курируемая, не курируемая)
И интегрированные базы данных, в которых вся информация (курируемая, не курируемая)
NCBI Entrez – доступ к информации о нуклеотидных и аминокислотных последовательностях и структурах
Ecocyc – все о E. coli – гены, белки, метаболизм и пр.
Теперь перейдем к рассмотрению инструментов биоинформатики. Инструменты определяются задачами, которые мы
Теперь перейдем к рассмотрению инструментов биоинформатики. Инструменты определяются задачами, которые мы
Основу биоинформатики составляют сравнения. Если у нас есть, например, аминокислотная последовательность, о которой у нас есть экспериментальные данные, и известны ее функции, и другая, похожая на нее последовательность, мы можем предположить, что эти последовательности выполняют сходные функции. Это задача поиска сходства последовательностей
Как сравнивают последовательности? Запишем одну последовательность под другой:
attgtACcTCgTgG-AA----
-----AC-TCaTaGcAAccag
Нам надо при сравнении
Как сравнивают последовательности? Запишем одну последовательность под другой:
attgtACcTCgTgG-AA----
-----AC-TCaTaGcAAccag
Нам надо при сравнении
Компьютерные технологии в науке, С.15-20.
Таким образом, первым делом после секвенирования последовательности ищут в базах данных
Таким образом, первым делом после секвенирования последовательности ищут в базах данных
Например, если лизин (положительно заряженная аминокислота заменится на лейцин (похожий по созвучию, но совершенно несходный по свойствам), то для пространственной структуры и функций белка это может оказаться катастрофой. А вот замена лизина на аргинин (также положительно заряженный) может не сказаться на структуре белка.
Поэтому при сравнении аминокислотных последовательностей учитывают также матрицу сопоставления аминокислотных остатков (похожих, менее похожих и совсем непохожих).
Молекулярно-генетические данные хранятся в специализированных банках данных (все на английском языке):
Молекулярно-генетические данные хранятся в специализированных банках данных (все на английском языке):
крупнейшая база генетических данных – GeneBank
удобная в навигации база генетических последовательностей – Ensembl
удобная в навигации база генетических последовательностей – Ensembl
удобный доступ к полным геномам через сайт Европейского института биоинформатики -
удобный доступ к полным геномам через сайт Европейского института биоинформатики -
крупнейший банк белковых данных – UniProt.org
крупнейший банк белковых данных – UniProt.org
крупнейший банк данных о структуре биологических макромолекул http://www.pdb.org/
крупнейший банк данных о структуре биологических макромолекул http://www.pdb.org/
Информационные системы, касающиеся моделей макромолекул и надмолекулярных структур:
GeneBank & EMBL
Информационные системы, касающиеся моделей макромолекул и надмолекулярных структур:
GeneBank & EMBL
PDB – пространственные структуры белков
Swiss-Prot – наиболее качественная база данных, содержащая аминокислотные последовательности белков
KEGG – информация о метаболизме (такая, которая представлена на карте метаболических путей)
SCOP – база данных структурной классификации белков (описывается структура белков)
PFAM – база данных по семействам белков
GO (Gene Ontology) – классификация генов (попытка создания набора терминов, упорядочивания терминологии)
ProDom – белковые домены
AsMamDB – альтернативный сплайсинг у млекопитающих
NCBI Entrez – доступ к информации о нуклеотидных и аминокислотных последовательностях и структурах
Ecocyc – все о E. coli – гены, белки, метаболизм и пр.
Accelrys Discovery Studio
Окно программы Discovery Studio
Видны вторичные и третичные структуры, поверхность белка
Окно программы Discovery Studio
Видны вторичные и третичные структуры, поверхность белка
CAZy: Carbohydrate-Active Enzymes Database.
На сайте представлена современная классификация ферментов синтеза и
CAZy: Carbohydrate-Active Enzymes Database. На сайте представлена современная классификация ферментов синтеза и
http://molbiol.edu.ru/review/01_01.html
http://molbiol.edu.ru/review/01_01.html
Форматы файлов, используемых в биоинформатике
FASTA
>roa1_drome Rea guano receptor type III >>
Форматы файлов, используемых в биоинформатике
FASTA
>roa1_drome Rea guano receptor type III >>
MVNSNQNQNGNSNGHDDDFPQDSITEPEHMRKLFIGGLDYRTTDENLKAHEKWGNIVDVVVMKDPRTKRSRGFGFITYSHSSMIDEAQKSRPHKIDGRVEPKRAVPRQDIDSPNAGATVKKLFVGALKDDHDEQSIRDYFQHFGNIVDNIVIDKETGKKRGFAFVEFDDYDPVDKVVLQKQHQLNGKMVDVKKALPKNDQQGGGGGRGGPGGRAGGNRGNMGGGNYGNQNGGGNWNNGGNNWGNNRGNDNWGNNSFGGGGGGGGGYGGGNNSWGNNNPWDNGNGGGNFGGGGNNWNGGNDFGGYQQNYGGGPQRGGGNFNNNRMQPYQGGGGFKAGGGNQGNYGNNQGFNNGGNNRRY
>roa2_drome Rea guano ligand
MVNSNQNQNGNSNGHDDDFPQDSITEPEHMRKLFIGGLDYRTTDENLKAHEKWGNIVDVVVMKDPTSTSTSTSTSTSTSTSTMIDEAQKSRPHKIDGRVEPKRAVPRQDIDSPNAGATVKKLFVGALKDDHDEQSIRDYFQHLLLLLLLDLLLLDLLLLDLLLFVEFDDYDPVDKVVLQK
QHQLNGKMVDVKKALPKNDQQGGGGGRGGPGGRAGGNRGNMGGGNYGNQNGGGNWNNGGNNWGNNRGNDNWGNNSFGGGGGGGGGYGGGNNSWGNNNPWDNGNGGGNFGGGGNNWNGGNDFGGYQQNYGGGPQRGGGNFNNNRMQPYQGGGGFKAGGGNQGNYGNNQGFNNGGNNRRY
GenBank
LOCUS SCU49845 5028 bp DNA PLN 21-JUN-1999
DEFINITION Saccharomyces cerevisiae TCP1-beta gene,
GenBank
LOCUS SCU49845 5028 bp DNA PLN 21-JUN-1999
DEFINITION Saccharomyces cerevisiae TCP1-beta gene,
(AXL2) and Rev7p (REV7) genes, complete cds.
ACCESSION U49845
VERSION U49845.1 GI:1293613
KEYWORDS .
SOURCE Saccharomyces cerevisiae (baker's yeast)
ORGANISM Saccharomyces cerevisiae
Eukaryota; Fungi; Ascomycota; Saccharomycotina; Saccharomycetes;
Saccharomycetales; Saccharomycetaceae; Saccharomyces.
REFERENCE 1 (bases 1 to 5028)
AUTHORS Torpey,L.E., Gibbs,P.E., Nelson,J. and Lawrence,C.W.
TITLE Cloning and sequence of REV7, a gene whose function is required for
DNA damage-induced mutagenesis in Saccharomyces cerevisiae
JOURNAL Yeast 10 (11), 1503-1509 (1994)
PUBMED 7871890
REFERENCE 2 (bases 1 to 5028)
AUTHORS Roemer,T., Madden,K., Chang,J. and Snyder,M.
TITLE Selection of axial growth sites in yeast requires Axl2p, a novel
plasma membrane glycoprotein
JOURNAL Genes Dev. 10 (7), 777-793 (1996)
PUBMED 8846915
REFERENCE 3 (bases 1 to 5028)
AUTHORS Roemer,T.
TITLE Direct Submission
JOURNAL Submitted (22-FEB-1996) Terry Roemer, Biology, Yale University, New
Haven, CT, USA
FEATURES Location/Qualifiers
source 1..5028
/organism="Saccharomyces cerevisiae"
/db_xref="taxon:4932"
/chromosome="IX"
/map="9"
CDS <1..206
/codon_start=3
/product="TCP1-beta"
/protein_id="AAA98665.1"
/db_xref="GI:1293614"
/translation="SSIYNGISTSGLDLNNGTIADMRQLGIVESYKLKRAVVSSASEA
AEVLLRVDNIIRARPRTANRQHM"
gene 687..3158
/gene="AXL2"
CDS 687..3158
/gene="AXL2"
/note="plasma membrane glycoprotein"
/codon_start=1
/function="required for axial budding pattern of S.
cerevisiae"
/product="Axl2p"
/protein_id="AAA98666.1"
/db_xref="GI:1293615"
/translation="MTQLQISLLLTATISLLHLVVATPYEAYPIGKQYPPVARVNESF
TFQISNDTYKSSVDKTAQITYNCFDLPSWLSFDSSSRTFSGEPSSDLLSDANTTLYFN
------------------------------------------//--------------------------------------------------------- YGSQKTVDTEKLFDLEAPEKEKRTSRDVTMSSLDPWNSNISPSPVRKSVTPSPYNVTK
RNRHLQNIQDSQSGKNGITPTTMSTSSSDDFVPVKDGENFCWVHSMEPDRRPSKKRL
VDFSNKSNVNVGQVKDIHGRIPEML"
gene complement(3300..4037)
/gene="REV7"
CDS complement(3300..4037)
/gene="REV7"
/codon_start=1
/product="Rev7p"
/protein_id="AAA98667.1"
/db_xref="GI:1293616"
/translation="MNRWVEKWLRVYLKCYINLILFYRNVYPPQSFDYTTYQSFNLPQ
FVPINRHPALIDYIEELILDVLSKLTHVYRFSICIINKKNDLCIEKYVLDFSELQHVD KDDQIITETEVFDEFRSSLNSLIMHLEKLPKVNDDTITFEAVINAIELELGHKLDRNR
RVDSLEEKAEIERDSNWVKCQEDENLPDNNGFQPPKIKLTSLVGSDVGPLIIHQFSEK
LISGDDKILNGVYSQYEEGESIFGSLF"
ORIGIN
1 gatcctccat atacaacggt atctccacct caggtttaga tctcaacaac ggaaccattg
61 ccgacatgag acagttaggt atcgtcgaga gttacaagct aaaacgagca gtagtcagct
121 ctgcatctga agccgctgaa gttctactaa gggtggataa catcatccgt gcaagaccaa
181 gaaccgccaa tagacaacat atgtaacata tttaggatat acctcgaaaa taataaaccg
241 ccacactgtc attattataa ttagaaacag aacgcaaaaa ttatccacta tataattcaa
301 agacgcgaaa aaaaaagaac aacgcgtcat agaacttttg gcaattcgcg tcacaaataa
------------------------------------------//----------------------------------------------
4621 tcttcgcact tcttttccca ttcatctctt tcttcttcca aagcaacgat ccttctaccc
4681 atttgctcag agttcaaatc ggcctctttc agtttatcca ttgcttcctt cagtttggct
4741 tcactgtctt ctagctgttg ttctagatcc tggtttttct tggtgtagtt ctcattatta
4801 gatctcaagt tattggagtc ttcagccaat tgctttgtat cagacaattg actctctaac
4861 ttctccactt cactgtcgag ttgctcgttt ttagcggaca aagatttaat ctcgttttct
4921 ttttcagtgt tagattgctc taattctttg agctgttctc tcagctcctc atatttttct
4981 tgccatgact cagattctaa ttttaagcta ttcaatttct ctttgatc
//
GenBank. Запись sequence
GenBank. Запись sequence
GenBank. Запись mRNA
GenBank. Запись mRNA
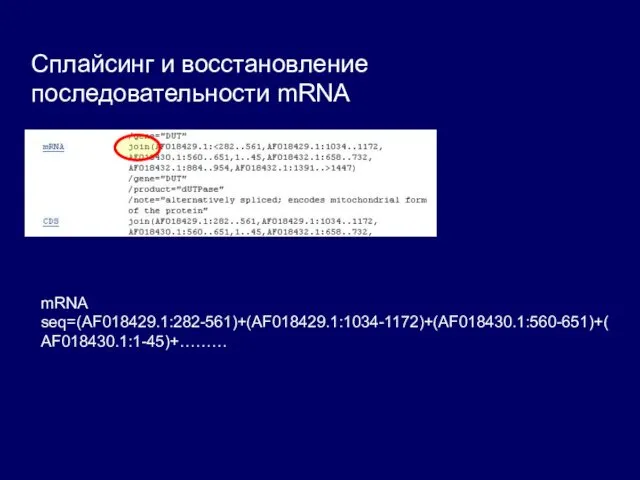
Сплайсинг и восстановление последовательности mRNA
mRNA seq=(AF018429.1:282-561)+(AF018429.1:1034-1172)+(AF018430.1:560-651)+(AF018430.1:1-45)+………
Сплайсинг и восстановление последовательности mRNA
mRNA seq=(AF018429.1:282-561)+(AF018429.1:1034-1172)+(AF018430.1:560-651)+(AF018430.1:1-45)+………
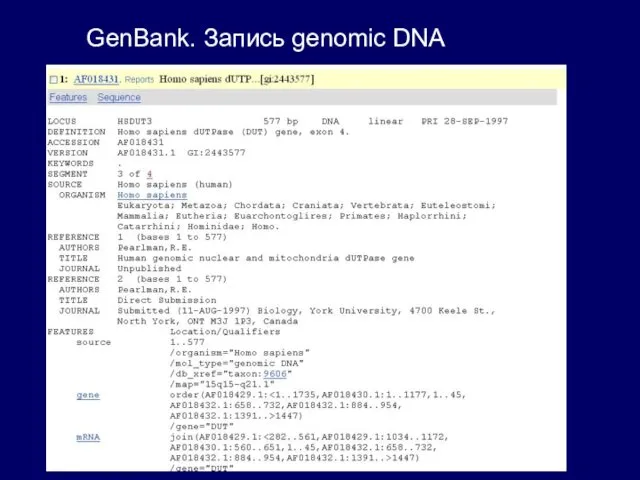
GenBank. Запись genomic DNA
GenBank. Запись genomic DNA
GenBank. Аннотация
GenBank. Аннотация
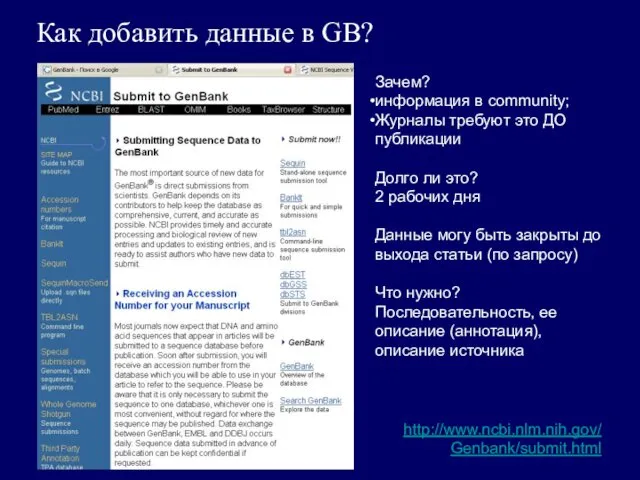
Как добавить данные в GB?
http://www.ncbi.nlm.nih.gov/
Genbank/submit.html
Зачем?
информация в community;
Журналы требуют это ДО публикации
Долго
Как добавить данные в GB?
http://www.ncbi.nlm.nih.gov/
Genbank/submit.html
Зачем?
информация в community;
Журналы требуют это ДО публикации
Долго
2 рабочих дня
Данные могу быть закрыты до выхода статьи (по запросу)
Что нужно?
Последовательность, ее описание (аннотация), описание источника
Форматы описания белков
PDB
PDB-XML
MMDB-Cn3D
Форматы описания белков
PDB
PDB-XML
MMDB-Cn3D
PDB – Protein Data Bank
HEADER LUMINESCENT PROTEIN 09-DEC-03 1RRX
TITLE CRYSTALLOGRAPHIC
PDB – Protein Data Bank
HEADER LUMINESCENT PROTEIN 09-DEC-03 1RRX
TITLE CRYSTALLOGRAPHIC
TITLE 2 FLUOROTYROSYL-GREEN FLUORESCENT PROTEIN
COMPND MOL_ID: 1;
COMPND 2 MOLECULE: SIGF1-GFP FUSION PROTEIN;
COMPND 3 CHAIN: A;
COMPND 4 ENGINEERED: YES;
COMPND 5 OTHER_DETAILS: CONTAINS 3-FLUORO-TYROSINE
SOURCE MOL_ID: 1;
SOURCE 2 ORGANISM_SCIENTIFIC: AEQUOREA VICTORIA;
SOURCE 3 ORGANISM_COMMON: FUNGI;
SOURCE 4 EXPRESSION_SYSTEM: ESCHERICHIA COLI;
SOURCE 5 EXPRESSION_SYSTEM_COMMON: BACTERIA;
SOURCE 6 EXPRESSION_SYSTEM_VECTOR_TYPE: PLASMID
KEYWDS BETA-BARREL, EGFP, NON-CANONICAL AMINO ACID, CHROMOPHORE
KEYWDS 2 ISOMERISATION
EXPDTA X-RAY DIFFRACTION
AUTHOR J.H.BAE,P.PARAMITA PAL,L.MORODER,R.HUBER,N.BUDISA
REVDAT 1 08-JUN-04 1RRX 0
JRNL AUTH J.H.BAE,P.PARAMITA PAL,L.MORODER,R.HUBER,N.BUDISA
JRNL TITL CRYSTALLOGRAPHIC EVIDENCE FOR ISOMERIC
JRNL TITL 2 CHROMOPHORES IN 3-FLUOROTYROSYL-GREEN FLUORESCENT
JRNL TITL 3 PROTEIN.
JRNL REF CHEMBIOCHEM V. 5 720 2004
JRNL REF 2 EUROP.J.CHEM.BIOL.
JRNL REFN GE ISSN 1439-4227
REMARK 1
REMARK 2
REMARK 2 RESOLUTION. 2.10 ANGSTROMS.
REMARK 3
REMARK 3 REFINEMENT.
--------------------------------------------//-----------------------------------------------------------
REMARK 500 M RES CSSEQI ATM1 ATM2 ATM3
REMARK 500 LEU A 44 CA - CB - CG ANGL. DEV. = 13.7 DEGREES
REMARK 500 LEU A 64 N - CA - C ANGL. DEV. =-16.6 DEGREES
REMARK 500 LEU A 64 CA - C - O ANGL. DEV. =-16.0 DEGREES
REMARK 500 LEU A 64 CA - C - N ANGL. DEV. = 31.6 DEGREES
REMARK 500 LEU A 64 O - C - N ANGL. DEV. =-15.9 DEGREES
REMARK 500 THR A 97 N - CA - C ANGL. DEV. =-14.0 DEGREES
REMARK 500 GLU A 115 N - CA - C ANGL. DEV. =-13.1 DEGREES
REMARK 900
REMARK 900 RELATED ENTRIES
REMARK 900 RELATED ID: 1EMG RELATED DB: PDB
REMARK 900 THE WILD TYPE OF STUDIED NON-CANONICAL AMINO ACID-
REMARK 900 CONTAINING GFP
DBREF 1RRX A 2 227 UNP P42212 GFP_AEQVI 290 517
SEQADV 1RRX YOF A 39 UNP P42212 TYR 327 MODIFIED RESIDUE
SEQADV 1RRX MFC A 66 UNP P42212 THR 353 MODIFIED RESIDUE
SEQADV 1RRX MFC A 66 UNP P42212 TYR 354 MODIFIED RESIDUE
SEQADV 1RRX MFC A 66 UNP P42212 GLY 355 MODIFIED RESIDUE
SEQADV 1RRX YOF A 74 UNP P42212 TYR 362 MODIFIED RESIDUE
SEQADV 1RRX YOF A 92 UNP P42212 TYR 380 MODIFIED RESIDUE
SEQADV 1RRX YOF A 106 UNP P42212 TYR 394 MODIFIED RESIDUE
SEQADV 1RRX YOF A 143 UNP P42212 TYR 431 MODIFIED RESIDUE
SEQADV 1RRX YOF A 143 UNP P42212 TYR 433 MODIFIED RESIDUE
SEQADV 1RRX YOF A 151 UNP P42212 TYR 439 MODIFIED RESIDUE
SEQADV 1RRX YOF A 182 UNP P42212 TYR 470 MODIFIED RESIDUE
SEQADV 1RRX YOF A 200 UNP P42212 TYR 488 MODIFIED RESIDUE
SEQRES 1 A 226 SER LYS GLY GLU GLU LEU PHE THR GLY VAL VAL PRO ILE
SEQRES 2 A 226 LEU VAL GLU LEU ASP GLY ASP VAL ASN GLY HIS LYS PHE
SEQRES 3 A 226 SER VAL SER GLY GLU GLY GLU GLY ASP ALA THR YOF GLY
SEQRES 4 A 226 LYS LEU THR LEU LYS PHE ILE CYS THR THR GLY LYS LEU
SEQRES 5 A 226 PRO VAL PRO TRP PRO THR LEU VAL THR THR LEU MFC VAL
SEQRES 6 A 226 GLN CYS PHE SER ARG YOF PRO ASP HIS MET LYS GLN HIS
SEQRES 7 A 226 ASP PHE PHE LYS SER ALA MET PRO GLU GLY YOF VAL GLN
SEQRES 8 A 226 GLU ARG THR ILE PHE PHE LYS ASP ASP GLY ASN YOF LYS
SEQRES 9 A 226 THR ARG ALA GLU VAL LYS PHE GLU GLY ASP THR LEU VAL
SEQRES 10 A 226 ASN ARG ILE GLU LEU LYS GLY ILE ASP PHE LYS GLU ASP
SEQRES 11 A 226 GLY ASN ILE LEU GLY HIS LYS LEU GLU YOF ASN YOF ASN
SEQRES 12 A 226 SER HIS ASN VAL YOF ILE MET ALA ASP LYS GLN LYS ASN
SEQRES 13 A 226 GLY ILE LYS VAL ASN PHE LYS ILE ARG HIS ASN ILE GLU
SEQRES 14 A 226 ASP GLY SER VAL GLN LEU ALA ASP HIS YOF GLN GLN ASN
SEQRES 15 A 226 THR PRO ILE GLY ASP GLY PRO VAL LEU LEU PRO ASP ASN
SEQRES 16 A 226 HIS YOF LEU SER THR GLN SER ALA LEU SER LYS ASP PRO
SEQRES 17 A 226 ASN GLU LYS ARG ASP HIS MET VAL LEU LEU GLU PHE VAL
SEQRES 18 A 226 THR ALA ALA GLY ILE
MODRES 1RRX YOF A 39 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 74 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 92 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 106 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 143 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 145 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 151 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 182 TYR 3-FLUOROTYROSINE
MODRES 1RRX YOF A 200 TYR 3-FLUOROTYROSINE
MODRES 1RRX MFC A 66 GLY CYCLIZED
MODRES 1RRX MFC A 66 TYR CYCLIZED
HETNAM YOF 3-FLUOROTYROSINE
HETNAM MFC 5-[1-(3-FLUORO-4-HYDROXY-PHENYL)-METH-(Z)-YLIDENE]-3,
HETNAM 2 MFC 5-DIHYDRO-IMIDAZOL-4-ONE
FORMUL 1 YOF 9(C9 H10 F N O3)
FORMUL 1 MFC C15 H16 F N3 O5
FORMUL 2 HOH *61(H2 O)
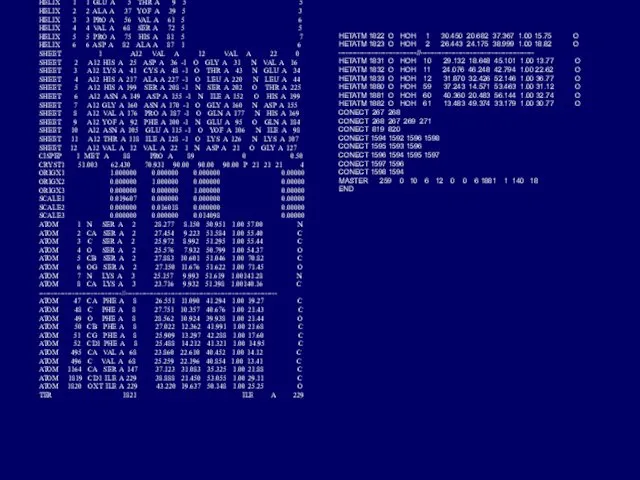
HELIX 1 1 GLU A 5 THR A 9 5 5
HELIX 1 1 GLU A 5 THR A 9 5 5
HETATM 1822 O HOH 1 30.450 20.682 37.367 1.00 15.75 O
HETATM 1823 O HOH 2 26.443 24.175 38.999 1.00 18.82 O
---------------------------------//------------------------------------------------
HETATM 1831 O HOH 10 29.132 18.648 45.101 1.00 13.77 O
HETATM 1832 O HOH 11 24.076 46.248 42.794 1.00 22.62 O
HETATM 1833 O HOH 12 31.870 32.426 52.146 1.00 36.77 O
HETATM 1880 O HOH 59 37.243 14.571 53.463 1.00 31.12 O
HETATM 1881 O HOH 60 40.360 20.483 56.144 1.00 32.74 O
HETATM 1882 O HOH 61 13.483 49.374 33.179 1.00 30.77 O
CONECT 267 268
CONECT 268 267 269 271
CONECT 819 820
CONECT 1594 1592 1596 1598
CONECT 1595 1593 1596
CONECT 1596 1594 1595 1597
CONECT 1597 1596
CONECT 1598 1594
MASTER 259 0 10 6 12 0 0 6 1881 1 140 18
END
PDB-XML
PDBML: the representation of archival macromolecular structure data in XML. John
PDB-XML
PDBML: the representation of archival macromolecular structure data in XML. John
xmlns:xsi="http://www.w3.org/2001/XMLSchema-instance"
xsi:schemaLocation="http://pdbml.pdb.org/schema/pdbx-v32.xsd pdbx-v32.xsd">



























 Биопластики: область применения
Биопластики: область применения Эмульсиялардың тұрақтылығына полиэтиленгликоль-баз композицияларының әсері
Эмульсиялардың тұрақтылығына полиэтиленгликоль-баз композицияларының әсері Кристаллография. История развития
Кристаллография. История развития Производство фенолформальдегидной смолы
Производство фенолформальдегидной смолы Обмен липидов. Классификация липидов
Обмен липидов. Классификация липидов Хімічний склад синтетичних миючих засобів та їх основні нормативно-технічні показники
Хімічний склад синтетичних миючих засобів та їх основні нормативно-технічні показники Химия элементов VA группы
Химия элементов VA группы Органические производные титана со связями Ti-O-C. Получение и свойства. Полимеры на их основе
Органические производные титана со связями Ti-O-C. Получение и свойства. Полимеры на их основе Алкины. Ацетилен – представитель алкинов.
Алкины. Ацетилен – представитель алкинов. Презентация по Химии "Основные сведения о строении атома" - скачать смотреть
Презентация по Химии "Основные сведения о строении атома" - скачать смотреть  Кислотность органических соединений. Типы химических реакций
Кислотность органических соединений. Типы химических реакций Эмульсии как лиофобные дисперсные системы
Эмульсии как лиофобные дисперсные системы Альдегиды. Раствор формальдегида. Гексаметилентетрамин (метенамин)
Альдегиды. Раствор формальдегида. Гексаметилентетрамин (метенамин) Нефть. Состав и свойства
Нефть. Состав и свойства «Знаки химических элементов. Относительная атомная масса химических элементов»
«Знаки химических элементов. Относительная атомная масса химических элементов»  Поверхностные явления
Поверхностные явления Фазовые равновесия в системе ограниченно смешивающихся жидкостей
Фазовые равновесия в системе ограниченно смешивающихся жидкостей Способы разделения смесей
Способы разделения смесей Химические предприятия Саратовской области
Химические предприятия Саратовской области 1oe_zanyatie (1)
1oe_zanyatie (1) Напій кока-кола. Активні інгредієнти кока-коли
Напій кока-кола. Активні інгредієнти кока-коли Адсорбция. Адсорбциондық тепе-теңдік
Адсорбция. Адсорбциондық тепе-теңдік Аминокислоты
Аминокислоты Роль нафти у сучасному світі Підготував учень 11 класу Войтюк Дмитро
Роль нафти у сучасному світі Підготував учень 11 класу Войтюк Дмитро  Новітні досягнення в хімії (9 клас)
Новітні досягнення в хімії (9 клас) Рідкі кристали Використання
Рідкі кристали Використання  Що ховається за цифрами? Харчові домішки
Що ховається за цифрами? Харчові домішки Алканы. Гомологический ряд предельных углеводородов
Алканы. Гомологический ряд предельных углеводородов