Содержание
- 2. Шаг 5: Анализ данных
- 3. Особенности программного обеспечения для анализа данных NGS Анализ данных NGS. Брагин Антон, Sequoia Genetics. 2013. Модульная
- 4. ДНК A Приготовление библиотеки B Секвенирование D Анализ данных
- 5. Анализ данных Ion Torrent Определение положений на чипе, в которых находятся последовательности Перевод последовательности сигналов в
- 6. Ошибки случаются… Эксперимент. Ошибки постановки эксперимента Биоинформатика. Ошибки в чтениях возникают из-за неточности работы секвенатора Контроль
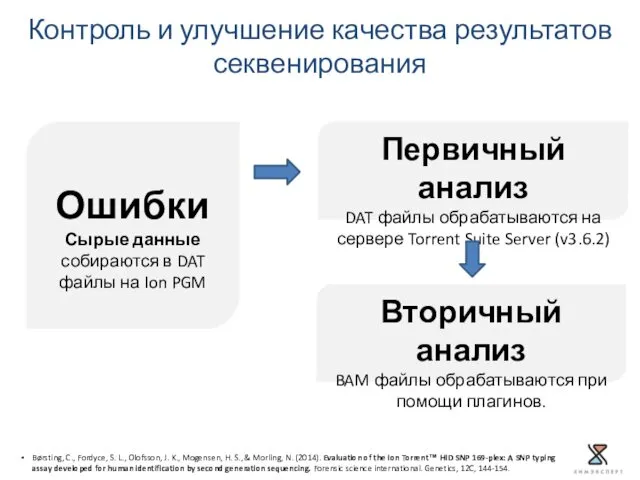
- 7. Контроль и улучшение качества результатов секвенирования Ошибки Сырые данные собираются в DAT файлы на Ion PGM
- 8. 1) Димеры адаптеров. Адаптеры соединяются друг с другом, без фрагмента ДНК образца Возможные ошибки Barry Merriman,
- 9. Возможные ошибки Barry Merriman, Ion Torrent R&D Team, Jonathan M. Rothberg. Progress in Ion Torrent semiconductor
- 10. Тримминг - удаление ошибок секвенирования Две задачи тримминга: 1. Удаление последовательности адаптера в чтениях 2. Отсечение
- 11. P – вероятность ошибки Q – параметр качества (Phred Quality Score) FASTQ – стандартный формат записи
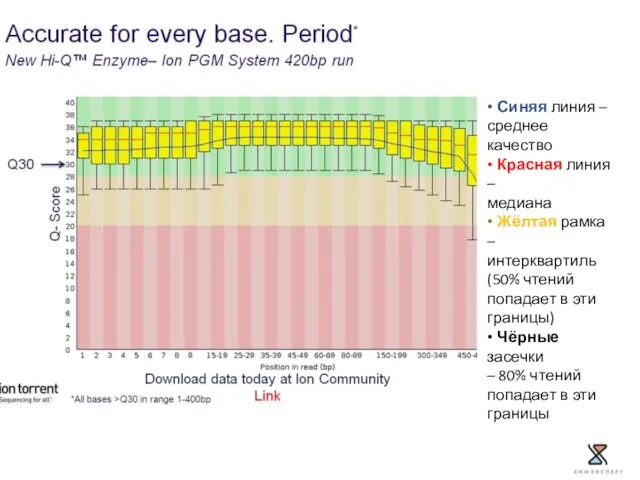
- 12. • Синяя линия – среднее качество • Красная линия – медиана • Жёлтая рамка – интерквартиль
- 13. FASTQ – общепринятый формат записи чтений. FASTQ – стандартный формат записи чтений Barry Merriman, Ion Torrent
- 14. Качество в формате FASTQ закодировано в ASCII – символах Существовало несколько стандартов записи качества Многим программам
- 15. Первичный анализ Børsting, C., Fordyce, S. L., Olofsson, J. K., Mogensen, H. S., & Morling, N.
- 16. Первичный анализ Børsting, C., Fordyce, S. L., Olofsson, J. K., Mogensen, H. S., & Morling, N.
- 17. Фильтры для ридов Варианты фильтрации прочтений: 1. Удаление коротких прочтений 2. Удаление димеров адаптеров 3. Удаление
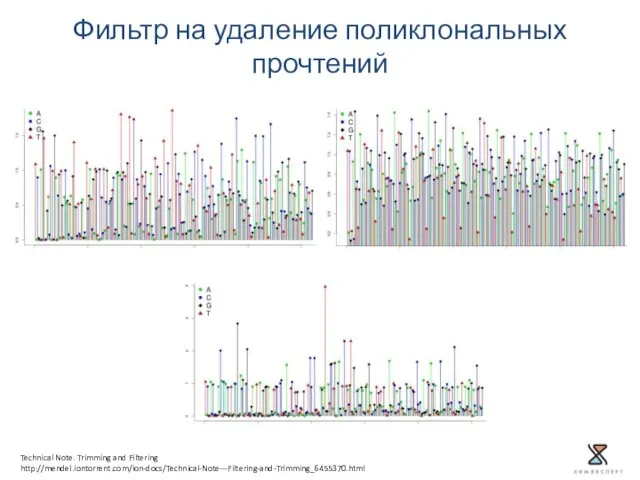
- 18. Фильтр на удаление поликлональных прочтений Technical Note. Trimming and Filtering http://mendel.iontorrent.com/ion-docs/Technical-Note---Filtering-and-Trimming_6455370.html
- 19. Torrent Suite™ Data Analysis Flow
- 20. Example shown for 100bp (260 flow) run on Ion PITM Chip (TAH-191) Ion Proton™ System Pipeline
- 21. Example shown for 100bp (260 flow) run on Ion PITM Chip (TAH-191) Ion Proton™ System Pipeline
- 22. Вторичный анализ (Обработка BAM файлов при помощи плагинов) Methods, tools, and pipelines for analysis of Ion
- 23. Шаг 1: Тримминг по качеству 3’ конца и Ion P1B адаптеру Шаг 2: Оценка и контроль
- 24. Анализ транскриптома. Рабочий процесс Life Technologies—Sample to RNA-Seq. 2012 Обсчет/статистика Картирование Оценка качества Предварительная обработка данных
- 25. Ion Proton™ System Enables High Quality Transcriptome Analysis with >80M Reads per Run Ion Proton™ Runs
- 26. Дополнительный шаг по обрезанию концов. Низкое качество и фрагменты адаптерной последовательности приводят к ошибкам картирования или
- 27. Программа FastQC использует FASTQ файл в качестве входных данных Качество прочтений по каждому нуклеотиду Оценка качества
- 28. Ошибки можно не только удалять, но и исправлять Коррекция чтений Программы, исправляющие ошибки, основаны на подсчёте
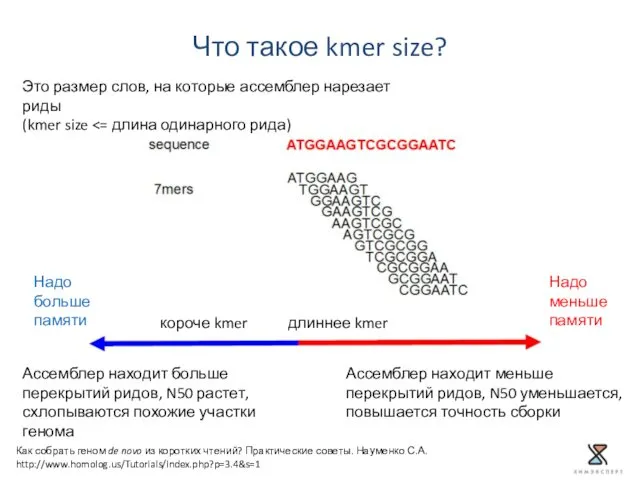
- 29. Что такое kmer size? Как собрать геном de novo из коротких чтений? Практические советы. Науменко С.А.
- 30. Для анализа транскриптома следует использовать параметр с длиной фрагмента для анализа 18 нуклеотидов (и количество допустимых
- 31. SAM-формат (Sequence Alignment/Map format) – текстовый формат, предназначенный для представления информация о картировании чтений. Значения отдельных
- 32. BAM-формат (Binary Sequence Alignment/Map) - Сжатый бинарный вариант формата SAM. Для быстрого доступа к данным по
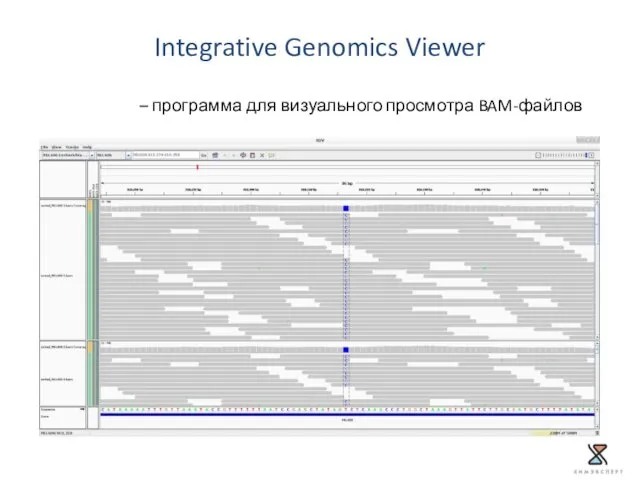
- 33. Integrative Genomics Viewer – программа для визуального просмотра BAM-файлов
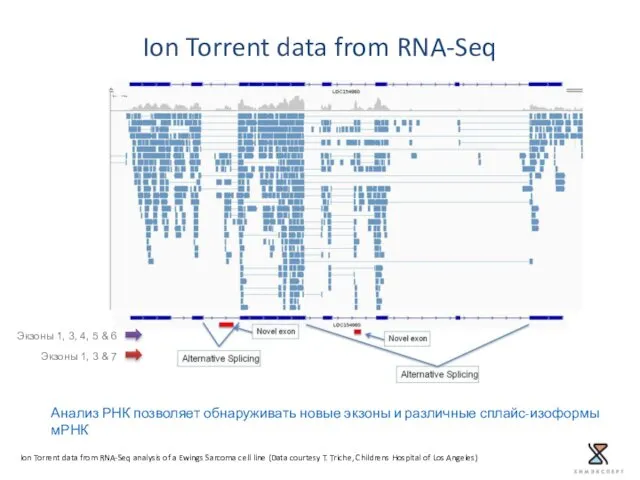
- 34. Ion Torrent data from RNA-Seq analysis of a Ewings Sarcoma cell line (Data courtesy T. Triche,
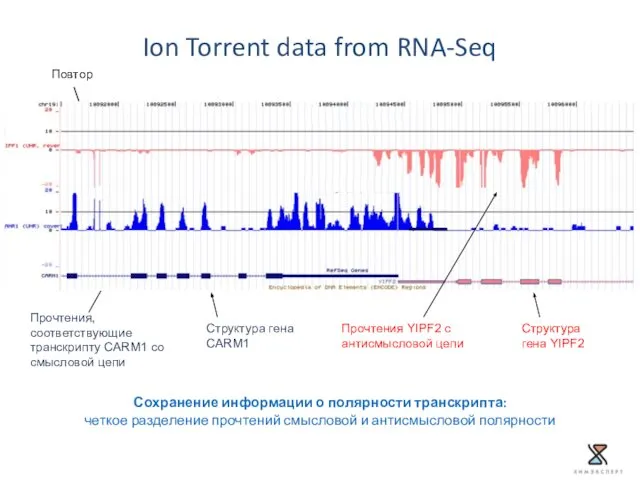
- 35. Повтор Прочтения YIPF2 с антисмысловой цепи Структура гена YIPF2 Структура гена CARM1 Прочтения, соответствующие транскрипту CARM1
- 36. EWSR1/FLI1 fusion protein type 1 (EWSR1/FLI1 fusion) mRNA Ion Torrent Internal Data Ion Torrent data from
- 37. Шаг 4: Подсчет картированных прочтений Скрипт htseq-count.py для подсчета картированных прочтений Скрипт – простая программа, предназначенная
- 38. Spike-in РНК: известна последовательность известна конечная концентрация используется для оценки точности измерений дифференциальной экспрессии генов 92
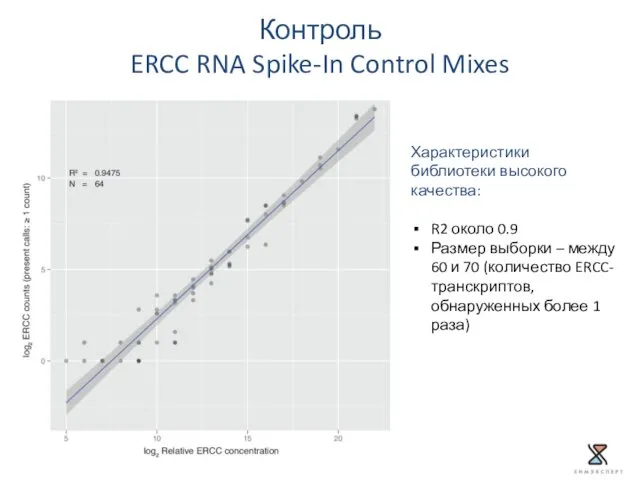
- 39. Контроль ERCC RNA Spike-In Control Mixes Характеристики библиотеки высокого качества: R2 около 0.9 Размер выборки –
- 40. TaqMan Expression Data with MAQC Ion Proton™ Expression Data with MAQC R2 = 0.958 N= 657
- 41. Высокий коэффициент корреляции с данными микрочипов Усредненные данные трех чипов 314 на образец РНК сравнивались с
- 42. Скрипт на Perl анализирует SAM файл на базовую статистику по картированию: общее количество картированных ридов, риды,
- 43. Нормализация данных RNA-Seq необходима из-за различий в глубине секвенирования, длине генов, отличий между образцами по количеству
- 44. Обобщенные статистические подходы к анализу транскриптомных данных и рекомендации по данному вопросу описаны в Current Protocols
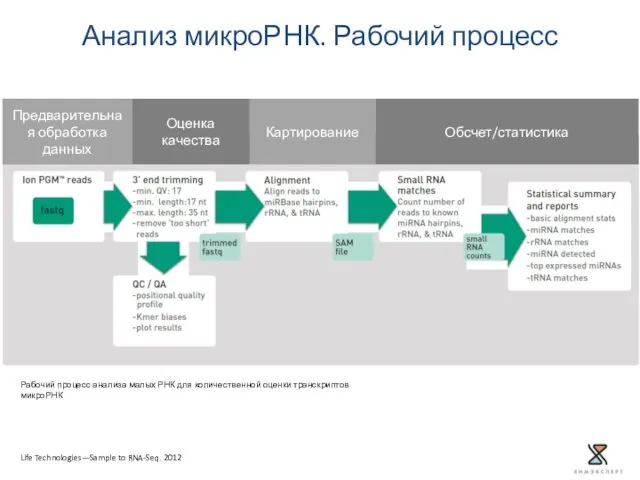
- 45. Анализ микроРНК. Рабочий процесс Life Technologies—Sample to RNA-Seq. 2012 Обсчет/статистика Картирование Оценка качества Предварительная обработка данных
- 46. FASTX-toolkit – программный пакет набора инструментов для обработки и оценки FASTQ файлов. fastq_quality_trimmer применяется таким же
- 47. Первый шаг картирования – шпильки микроРНК. Предшественники микроРНК (60-90 нуклеотидов) хранятся в базе RFAM miRBase database
- 48. Шаг 4: Подсчет картированных прочтений Скрипт htseq-count.py для подсчета картированных прочтений Что делает: из SAM-файла извлекает
- 49. Скрипт на Perl анализирует SAM файл на базовую статистику по картированию: общее количество картированных ридов, риды,
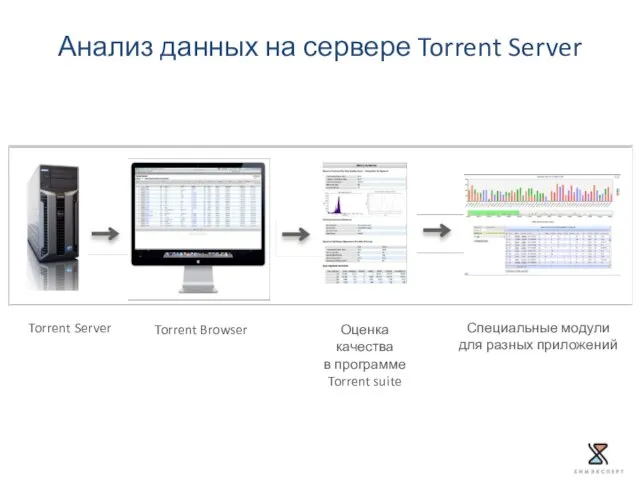
- 50. Torrent Server Torrent Browser Оценка качества в программе Torrent suite Специальные модули для разных приложений Анализ
- 51. Облако Biological Interpretation Partek® Genomics Suite™ Partek® Flow™ Partek® Pathway™ Сырые данные Copyright © 2011 Partek
- 52. Характеристики Интеграция с Torrent Suite™ Software Работает в облаке и на кластере Online доступ к данным
- 53. Количественное картирование транскриптома Обнаружение новых транскриптов Использование всех доступных баз данных Оценка представленности отдельных изоформ Анализ
- 55. Скачать презентацию










































 Локальные вычислительные сети и их виды. Локальные вычислительные сети и их виды. Основные требования, предъявляемые к локал
Локальные вычислительные сети и их виды. Локальные вычислительные сети и их виды. Основные требования, предъявляемые к локал Устройство компьтера
Устройство компьтера Проектная деятельность на уроках информатики
Проектная деятельность на уроках информатики Архитектура, принципы построения современных вычислительных систем и комплексов. Вычислительные комплексы и сети систем РКО
Архитектура, принципы построения современных вычислительных систем и комплексов. Вычислительные комплексы и сети систем РКО АЛГОРИТМЫ В НАШЕЙ ЖИЗНИ урок информатики в 5 классе Учитель математики : Смолина Т.Г.
АЛГОРИТМЫ В НАШЕЙ ЖИЗНИ урок информатики в 5 классе Учитель математики : Смолина Т.Г. Қолданбалы программалар пакеті. Программалық жабдықтар
Қолданбалы программалар пакеті. Программалық жабдықтар Электронные таблицы Microsoft Excel
Электронные таблицы Microsoft Excel Инструменты и методы разработки интернет-проектов
Инструменты и методы разработки интернет-проектов Автоматизация комплекса задач менеджера отдела логистики ООО Эпсилон на платформе MS Access
Автоматизация комплекса задач менеджера отдела логистики ООО Эпсилон на платформе MS Access Занимательные задачи информатики. Задачи о лжецах
Занимательные задачи информатики. Задачи о лжецах Як ми виграли комп‘ютер. Гра-тест
Як ми виграли комп‘ютер. Гра-тест ИСПОЛЬЗОВАНИЕ СОВРЕМЕННЫХ ИНФОРМАЦИОННЫХ И КОММУНИКАЦИОННЫХ ТЕХНОЛОГИЙ В ОБРАЗОВАНИИ Презентация учебной дисциплины Москва -200
ИСПОЛЬЗОВАНИЕ СОВРЕМЕННЫХ ИНФОРМАЦИОННЫХ И КОММУНИКАЦИОННЫХ ТЕХНОЛОГИЙ В ОБРАЗОВАНИИ Презентация учебной дисциплины Москва -200 Кодирование
Кодирование Как делать анимацию
Как делать анимацию СРС-2
СРС-2 Blind date
Blind date Презентация "креативные индустрии" - скачать презентации по Информатике
Презентация "креативные индустрии" - скачать презентации по Информатике Автоматизированные системы, интенсивно использующие ПО
Автоматизированные системы, интенсивно использующие ПО Процессы и задачи. Операционные системы. Лекция 2
Процессы и задачи. Операционные системы. Лекция 2 Использование версии 30 ПИ Судебное делопроизводство ГАС Правосудие
Использование версии 30 ПИ Судебное делопроизводство ГАС Правосудие Команды mmx/xmm
Команды mmx/xmm Компьютерные сети
Компьютерные сети Кодирование текстовой информации
Кодирование текстовой информации MagicDiagram.com
MagicDiagram.com Информатика в играх и задачах. Основы логики. 2 класс ( 1 урок)
Информатика в играх и задачах. Основы логики. 2 класс ( 1 урок) Алгоритмизация и программирование. Понятие, свойства и способы записи алгоритмов. (Тема 5)
Алгоритмизация и программирование. Понятие, свойства и способы записи алгоритмов. (Тема 5) Проектирование баз данных
Проектирование баз данных Среда программирования Scratch. Занятие 3
Среда программирования Scratch. Занятие 3